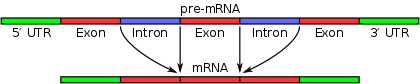
En intron är en icke‑kodande nukleotidsekvens i en gen som avlägsnas ur pre‑mRNA under bearbetningen till moget RNA. Termen intron används både om DNA‑sekvensen i genen och om motsvarande sekvens i det transkriberade RNA‑molekylen.
Mallar: introner och exoner
Exoner är de sekvenser som blir kvar i det mogna RNA efter RNA‑splicing och som vanligtvis kodar för aminosyror i den slutliga polypeptiden. Vissa exoner innehåller också icke‑kodande regioner (t.ex. UTR) som reglerar mRNA‑stabilitet och translation.
- Introner: delar av en gen som i normal splicing kasseras — icke‑kodande sekvenser.
- Exoner: delar av en gen som uttrycks — sekvenser som kodar för aminosyrasekvenser i ett protein.
Mekanism för RNA‑splicing
Efter transkription behandlas pre‑mRNA av splicingmaskineriet för att avlägsna introner innan eventuell översättning. Hos majoriteten av eukaryoter sker splicing i ett stort RNP‑komplex kallat spliceosomen, som består av små nukleära RNA (snRNA) och associerade proteiner (snRNPs, t.ex. U1, U2, U4/U6, U5). Spliceosomen känner igen korta konsensussekvenser vid intronets ändar (vanligtvis 5′-donor ofta med GU, 3′-acceptor ofta med AG) och en branch‑point A som deltar i katalysen av två transesterifieringssteg som sammanfogar exoner och frigör intronet som en lariat‑struktur.
Förutom spliceosomen finns även katalytiska (självsplicing) introner, framför allt grupp I och grupp II, som kan katalysera splicing utan proteinsubstanser — ett viktigt bevis på RNA:s katalytiska förmåga.
Alternativ splicing och biologisk betydelse
Alternativ splicing gör det möjligt för en och samma gen att ge upphov till flera olika mRNA‑isoformer och därigenom olika proteiner. Vanliga former av alternativ splicing är exonskippning, alternativ användning av 5′‑ eller 3′‑splice‑sites, intronretention och ömsesidigt uteslutna exoner. Alternativ splicing ökar proteomets mångfald och spelar en central roll i cell‑ och vävnadsspecifik reglering.
Introner kan även bära regulatoriska element (promotorfragment, enhancers, mikroRNA‑gener), bidra till exon‑shuffling under evolutionen och påverka genuttryck genom att påverka transkriptionstakt, mRNA‑export och nedbrytning.
Förekomst, längd och evolution
Introner förekommer i gener hos de flesta eukaryoter och i många virus; de kan finnas i gener för proteiner, ribosomalt RNA (rRNA) och överförings‑RNA (tRNA). Antalet och längden på introner varierar kraftigt mellan organismer: däggdjursgener innehåller ofta många och långa introner, medan encelliga eukaryoter som jäst har betydligt färre och kortare introner. Diskussioner om intronernas ursprung har lett till hypoteserna "intron‑early" och "intron‑late" — hur tidigt i evolutionen introner uppstod och spreds.
Klinisk betydelse och forskning
Mutationer som påverkar spliceosomens igenkänning eller intronernas konsensussekvenser kan leda till felaktig splicing och orsaka sjukdomar (till exempel vissa ärftliga sjukdomar och cancer). Therapeutiska metoder som antisense‑oligonukleotider kan riktas mot splicing för att korrigera eller modulera genuttryck.
Vanliga metoder för att studera introner och splicing är RT‑PCR, Northern blot, reporter‑assays och storskaliga metoder som RNA‑seq som kartlägger splicingmönster genomsnittligt över hela transkriptomet.
Historik
Upptäckten av introner vid slutet av 1970‑talet förändrade vår syn på geners struktur. Denna upptäckt belönades med Nobelpriset i fysiologi eller medicin 1993 till Phillip Sharp och Richard Roberts fick. Termen intron myntades av den amerikanske biokemisten Walter Gilbert.
Sammanfattningsvis är introner mer än bara "icke‑funktionella" avsnitt — de är dynamiska element i genomet med både reglerande roller och stor betydelse för evolution, genuttryck och sjukdom.